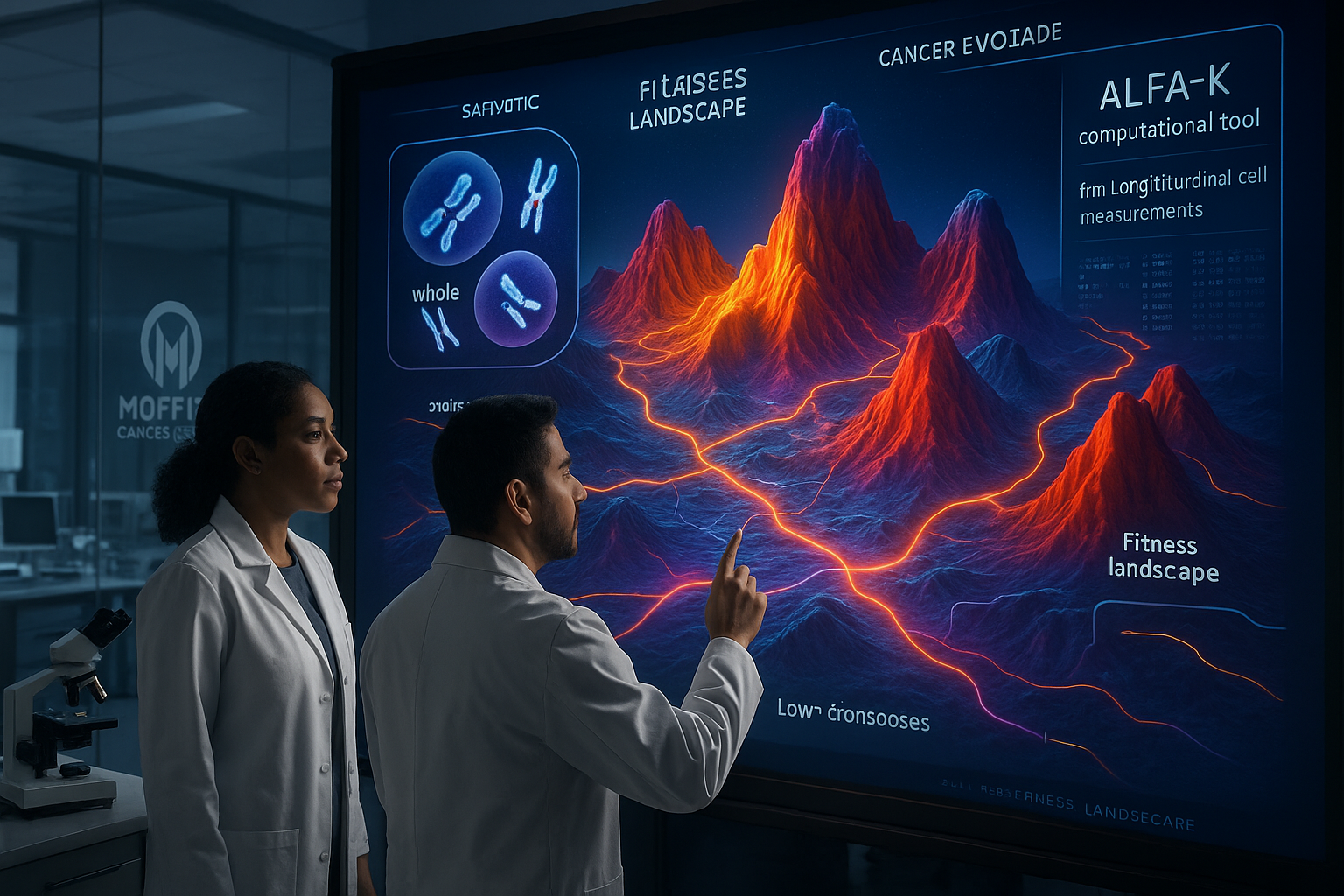
Cientistas do Moffitt Cancer Center relatam o desenvolvimento de um método computacional, ALFA-K, que usa medições de células únicas longitudinais para inferir como ganhos e perdas de cromossomos inteiros podem moldar o caminho evolutivo de um tumor. O trabalho, publicado na Nature Communications, argumenta que essas mudanças cromossômicas em grande escala seguem padrões mensuráveis influenciados pelo contexto celular e estresse relacionado ao tratamento, em vez de se desenrolarem como pura aleatoriedade.
O câncer pode evoluir rapidamente quando as células ganham ou perdem cromossomos inteiros—mudanças em grande escala que alteram a dosagem de muitos genes de uma só vez e podem remodelar como um tumor cresce e responde ao estresse. Pesquisadores do H. Lee Moffitt Cancer Center & Research Institute descrevem uma nova abordagem computacional, chamada ALFA-K (Adaptive Local Fitness landscapes for Aneuploid Karyotypes), que visa prever como tais mudanças no nível de cromossomos se acumulam ao longo do tempo. A equipe diz que o ALFA-K é projetado para dados de células únicas longitudinais, permitindo reconstruir como populações de células cancerosas se movem através de diferentes “estados” cromossômicos e estimar quais combinações de cromossomos parecem favorecidas sob pressões seletivas, incluindo estresse relacionado ao tratamento. Em um Q&A que acompanha o lançamento, a autora correspondente Noemi Andor disse que o objetivo era ir além de instantâneos únicos da genética tumoral e quantificar quais combinações de cromossomos ajudam as células a persistir. “O câncer evolui. À medida que os tumores crescem, suas células cometem erros constantemente ao copiar e dividir seu DNA. Muitos desses erros envolvem ganhar ou perder cromossomos inteiros”, disse Andor. De acordo com os pesquisadores, o ALFA-K difere de abordagens anteriores que frequentemente tratavam ganhos ou perdas individuais de cromossomos como tendo efeitos fixos. Em vez disso, modela a dependência de contexto—a mesma mudança cromossômica pode ser vantajosa ou prejudicial dependendo da composição cromossômica existente da célula—e incorpora instabilidade cromossômica contínua. No estudo, a equipe relata estimar a aptidão em mais de 270.000 configurações cromossômicas distintas, e conclui que condições ambientais e tratamento com cisplatina podem alterar o impacto na aptidão de mudanças no número de cópias cromossômicas. A análise também destaca o duplicação do genoma inteiro—quando uma célula duplica todos os seus cromossomos—como um mecanismo que pode amortecer alguns dos danos da instabilidade cromossômica extrema, com os pesquisadores descrevendo um limiar além do qual a duplicação genômica se torna evolutivamente vantajosa. O artigo lista Richard J. Beck, Tao Li e Noemi Andor como autores e foi publicado online na Nature Communications no final de dezembro de 2025. O trabalho foi apoiado pelo U.S. National Cancer Institute, incluindo as bolsas 1R37CA266727-01A1, 1R21CA269415-01A1 e 1R03CA259873-01A1. Os pesquisadores dizem que, no longo prazo, ferramentas como ALFA-K poderiam apoiar estratégias de tratamento “conscientes da evolução”—usando amostragem repetida como biópsias para identificar quando os tumores podem estar se aproximando de transições evolutivas arriscadas e selecionar terapias destinadas a limitar rotas para resistência a medicamentos.